루이지 리차르디 1 , 로사 마제오 2,* © , 안젤로 라ff알레 마르코트리지아노 1 , 굴리엘모 라이날디 3 , 파올로 이오비에노 4 , 비토 조노 1 , 스테파노 파반 1 © 그리고 콘체타 로티 2,*
- 1 토양, 식물 및 식품 과학부, 식물 유전학 및 육종 단위 University of Bari, Via Amendola 165/A, 70125 Bari, Italy; luigi.ricciardi@uniba.it (LR);angelo.marcotrigiano@uniba.it (팔); vito.zonno@uniba.it (VZ); stefano.pavan@uniba.it (SP)
- 2 농업, 식품 및 환경 과학부, University of Foggia, Via Napoli 25, 71122 Foggia, Italy
- 3 바리 대학교, Via Orabona 4, 70125 Bari, Italy; guglielmo.rainaldi@uniba.it
- 4 에너지 기술부, 바이오에너지, 바이오리파이너리 및 녹색 화학 부문, ENEA Trisaia Research Center, SS 106 Ionica, km 419+500, 75026 Rotondella(MT), Italy; paolo.iovieno@enea.it
* 일치: rosa.mazzeo@unifg.it (RM); concetta.lotti@unifg.it (CL)
요약 :
양파 (부추속 세파 L.)은 전 세계적으로 두 번째로 중요한 채소 작물이며 건강상의 이점으로 널리 알려져 있습니다. 양파의 경제적 중요성과 기능성 식품으로서의 가치에도 불구하고 양파는 유전적 다양성과 관련하여 제대로 조사되지 않았습니다. 여기에서 우리는 Bari 지방(이탈리아 남부 Apulia)의 작은 마을에서 11년의 재배 역사를 가진 토종종인 "Acquaviva red onion"(ARO)의 유전적 변이를 조사했습니다. 13개의 미세위성 마커 세트를 사용하여 XNUMX개의 ARO 집단과 XNUMX개의 일반적인 상업용 유형으로 구성된 생식질 컬렉션의 유전적 변이를 조사했습니다. 매개변수 및 비모수적 방법으로 유전자 구조를 분석한 결과 ARO는 잘 정의된 유전자 풀을 나타내며 종종 오해를 받는 Tropea 및 Montoro 랜드레이스와는 분명하게 구별됩니다. 일반적으로 신선 소비에 사용되는 구근에 대한 설명을 제공하기 위해 용해성 고형분 함량과 매운맛을 평가하였으며, ARO에서 위에서 언급한 두 가지 랜드레이스에 비해 더 높은 단맛을 보였다. 전반적으로, 본 연구는 상업 사기를 제한하고 소농의 소득을 향상시키는 데 기여할 수 있는 품질 라벨을 통해 촉진될 수 있는 ARO의 미래 가치 평가에 유용합니다.
개요
부추속(Allium) 속에는 약 750종[1]이 포함되며, 그 중 양파(Allium cepa L., 2n = 2x =16)가 가장 널리 퍼져 있는 것 중 하나입니다. A. cepa는 97.9년 주기와 교배 번식 행동을 가지고 있습니다. 오늘날 양파는 전 세계 생산량(2만 톤)으로 토마토에 이어 두 번째로 중요한 채소 작물입니다[1550]. 예로부터 양파 구근은 음식과 민간 약재로 사용되었습니다. 실제로 고대 이집트인들은 이미 기원전 3년의 의료용 파피루스 코덱스 에버스(Codex Ebers)에서 마늘과 양파의 사용을 기반으로 한 여러 치료 공식을 보고했습니다[XNUMX].
이 다재다능하고 건강한 야채는 날것으로, 신선하게 또는 가공 제품으로 섭취하며 많은 요리의 맛을 향상시키는 데 사용됩니다. 최근 여러 연구에서 양파 섭취가 심혈관 질환[4,5], 비만[6], 당뇨병[7] 및 다양한 형태의 암[8-10]의 위험을 줄일 수 있다고 주장합니다. 양파가 건강에 좋은 이유는 플라보노이드와 알크(엔)일 시스테인 설폭사이드(ACSO)라는 두 가지 종류의 기능식품 화합물의 높은 수준에 기인하는 경우가 많습니다. 첫 번째 클래스에는 플라보놀과 안토시아닌이 포함됩니다. 케르세틴은 자유 라디칼 소거 및 전이 금속 이온 결합에서 강력한 항산화 및 항염증 특성으로 알려진 주요 검출 가능한 플라보놀입니다. [11]; 반면 안토시아닌은 일부 양파 품종에 적색/보라색을 부여합니다. ACSO의 경우 가장 풍부한 것은 isoalliin [(+)-trans-S-1-propenyl-L-cysteine sulfoxide]입니다. [12], 양파의 매운 향과 맛을 간접적으로 담당하는 세포에 저장된 비휘발성 및 비단백질 생성 황 아미노산 [13]. 조직이 파괴되면 isoalliin은 효소 alliinase에 의해 절단되어 찢어짐을 유발하고 불쾌한 냄새를 유발하는 일련의 휘발성 화합물(pyruvate, 암모니아, thiosulphonate 및 propanethial S-oxide)을 생성합니다. [14]. 양파의 매운맛은 종종 가수분해에 의해 생성된 피루브산의 신선한 중량 그램당 양으로 측정됩니다. [15,16].
지중해 유역 국가에서 XNUMX 차 다양성 센터 중 하나로 제안 A. 세파 [17,18], 양파 구근은 모양, 크기, 색상, 건조 물질 및 매운맛이 매우 다양합니다. [19-하나]. 더욱이, 유황 기반 비료, 농업 관행, 토양 유형, 기후 조건, 품종 또는 토종 품종의 유전자형은 독특한 관능적 및 영양적 가치를 부여함으로써 구근 품질에 영향을 미칠 수 있습니다. [23-하나]. 이탈리아에서는 광범위한 양파 생식질 이용 가능성에도 불구하고 소수의 양파 품종만이 종종 과학적 연구의 대상이 되고 적절하게 특성화됩니다. [28,29].
농업 생물다양성의 철저한 유전 및 표현형 특성화는 식물 유전자원의 적절한 보존을 보장하고 가치 사슬에서 특정 유전자형의 사용을 촉진하는 데 중요합니다. [30-하나]. 단순 시퀀스 반복(SSR) 마커는 매핑을 위해 자주 선택되었습니다. [33-하나], DNA 지문 및 품종 식별 [36-하나], 그리고 랜드레이스 내 및 종족 간의 유전적 다양성에 대한 신뢰할 수 있는 추정 [39-하나], 유전자좌 특이적, 다중 대립 유전자, 공동 유전, 높은 재현성 및 자동화된 유전자형에 적합하기 때문입니다.
본 연구에서는 Bari 주의 Acquaviva delle Fonti 마을의 작은 지역에서 유기농법으로 재배되는 Apulian 전통 토종종인 “Acquaviva red onion”(ARO)에 주목했습니다. (Apulia, 남부 이탈리아). 이 랜드레이스의 구근은 크고 납작하며 붉은 색을 띠며 주로 지역 요리에 사용됩니다. ARO가 "Slow Food Presidium" 품질 마크를 획득했지만, 그 생산은 PGI(Protected Geographic Indication) 및 POD(Protected Designation of Origin)와 같은 유럽 연합 품질 마크에 의해 더욱 촉진되고 보호될 수 있습니다. 상업 사기를 방지하고 소규모 자영업자의 소득을 개선합니다. 여기에서 SSR 분자 마커는 ARO 개체군 간의 유전적 변이를 평가하고 다른 두 남부 이탈리아 적양파 품종과 이 품종을 구별하기 위한 강력한 도구로 사용되었습니다. 또한 시장 수요와 관련하여 ARO 향미를 평가하기 위해 매운맛과 용해성 고형분을 추정했습니다.
결과
Acquaviva 적양파 생식질 수집 및 형태적 특성화 구축
BiodiverSO Apulia 지역 프로젝트의 틀에서 농부들에 의해 기증된 ARO 랜드레이스의 13개 집단의 종자는 ARO 생식질 수집을 설정하는 데 사용되었습니다.
구근, 피부 및 과육과 관련된 형태학적 설명은 ARO 생식질 및 XNUMX개의 양파 랜드레이스에서 수집되었으며, XNUMX개는 "트로페아 적양파"(TRO) 랜드레이스에, XNUMX개는 "몬토로 구리 양파"(MCO) 랜드레이스에 속합니다(그림 1). 모든 ARO 전구는 납작했고 붉은색 외피와 살과 붉은 색조가 다른 것이 특징이었습니다. 대조적으로, TRO 전구의 살은 완전히 붉은색인 반면, MCO 전구의 살은 잘 착색되지 않았습니다(표 S1). 생화학적 분석을 통해 가용성 고체 함량과 매운맛을 평가할 수 있습니다. 표에 보고된 바와 같이 1, ARO 집단에서 구근의 고형 가용성 함량의 평균 값은 7.60이었고 6.00(ARO12)에서 9.50° Brix(ARO11 및 ARO13) 범위였습니다. 이 값은 TRO 및 MCO 육상 경주(각각 4.25 및 6.00° Brix)에 대해 추정된 값보다 높았습니다.

테이블 1. "Acquaviva Red Onion"(ARO), "Tropea Red Onion"(TRO) 및 "Montoro Copper Onion"(MCO) 모집단에서 평가된 고용체 함량 및 자극성 값 *.
| CODE | 가용성 고체 함량(Brix) | 매운맛(p몰그-1FW) | ||
| Mean | CV y (%) | Mean | CV y (%) | |
| ARO1 | 6.25D * | 5.65 | 5.84ab * | 23.78 |
| ARO2 | 7.25 DC | 4.87 | 6.51 | 22.98 |
| ARO3 | 7.50 BCD | 9.42 | 5.28 ab | 22.88 |
| ARO4 | 7.50 BCD | 0.00 | 6.97 | 3.74 |
| 바로 가기 5 | 7.50 BCD | 0.00 | 6.80 | 9.68 |
| ARO6 | 6.25 D | 5.65 | 4.51 ab | 39.18 |
| ARO7 | 7.25 DC | 4.87 | 5.25 ab | 15.44 |
| ARO8 | 9.00 AB | 0.00 | 7.04 | 3.49 |
| ARO9 | 8.25년 ABC | 4.28 | 6.84 | 0.15 |
| ARO10 | 7.00 DC | 0.00 | 5.94 ab | 6.57 |
| ARO11 | 9.50 | 7.44 | 5.54 ab | 16.43 |
| ARO12 | 6.00 D | 0.00 | 4.91 ab | 9.70 |
| ARO13 | 9.50 | 7.44 | 6.63 | 24.93 |
| MCO | 6.00 D | 0.00 | 4.18 ab | 2.66 |
| 트로1 | 4.25 E | 8.31 | 2.80의 B | 2.10 |
| 트로2 | 4.25 E | 8.31 | 4.28 ab | 4.79 |
* 대문자 또는 소문자가 동일한 의미는 각각 0.01P 또는 0.05P에서 통계적으로 다르지 않습니다(SNK's Test). y 변동 계수.
피루브산 함량으로 평가한 ARO 매운맛의 평균값은 6.00이었고 범위는 4.51pmol g입니다.-1 FW(ARO6) ~ 7.04(ARO8). 이 값은 TRO 및 MCO 랜드레이스(3.54 pmol g-1 FW 및 4.18pmol g-1 FW).
SSR 다형성과 접근 간의 유전적 관계
현재 연구에서 11개의 테스트된 SSR 프라이머 조합 중 37개가 단일 유전자좌 다형성, 즉 단일 개체에서 최대 55개의 증폭 산물을 제공했습니다. 전체적으로, 320(ACM2 및 ACM 147)에서 504(ACM11) 범위의 유전자좌당 대립유전자 수와 132개 대립유전자의 평균값으로 5명의 개인에서 XNUMX개의 대립유전자가 검출되었습니다(표 2). 개별 집단에서 대립유전자(Na)의 수는 1.94(ACM147 및 ACM504)에서 5.38(ACM132) 사이인 반면, 유효 대립유전자(Ne) 수는 1.41(ACM152)에서 2.82(ACM449) 사이였습니다. 불일치 Na와 Ne 값 사이의 값은 인구에서 빈도가 낮은 대립 유전자의 존재와 소수의 대립 유전자의 우세 때문입니다. 가장 높은 관찰된 이형접합체(Ho) 값은 ACM138 및 ACM449(0.62)에 대해 강조 표시된 반면, 가장 낮은 값은 ACM152(0.25)와 연관되었습니다. Panmictic 인구의 이론적 기대치에 해당하는 기대 이형 접합성(He)은 0.37(ACM504)에서 0.61(ACM132, ACM138 및 ACM449) 범위였습니다. Wright의 고정 지수(Fis)는 모든 마커에 대해 0.05에 가까운 값(평균 0.48)을 표시했으며, 이종 교배 종에 대해 예상되는 바와 같이 관찰된 이형 접합 수준과 예상되는 이형 접합 수준 사이의 유사한 값을 나타냅니다. 유전자 지문에서 개별 SSR 마커의 효율성은 PIC(다형성 정보 함량) 지수에 의해 추정되었으며, 평균 값은 0.33이고 범위는 504(ACM0.67)에서 132(ACM0.84)입니다. 또 다른 효율성 지수인 Shannon의 정보 지수(I)는 0.45의 평균값을 표시했으며 가정된 값의 범위는 152(ACM1.20)에서 132(ACMXNUMX)입니다.
테이블 2. ARO, TRO 및 MCO 집단에서 유전적 다양성을 추정하는 데 사용되는 11개의 SSR 마커의 다형성 특징. 총 대립유전자 수(Na), 밴드 크기 범위 및 다형성 정보 함량(PIC) 색인 이 연구에서 유전자형이 지정된 320명의 개인의 총 세트를 참조하십시오. 대립형질 수(Na), 유효 대립형질 수(Ne), 관찰된 이형접합체(Ho), 예상 이형접합체(He), 고정 지수(F)is), 그리고 Shannon의 정보 지수(I)는 각각 16명의 개인으로 구성된 20명의 인구에서 계산된 평균 값을 나타냅니다.
| 현장. | 총 나 | 크기 범위(bp) | PIC | Mean | |||||
| Na | Ne | Ho | He | I | Fis | ||||
| ACM91 | 4 | 189-205 | 0.40 | 2.63 | 1.72 | 0.38 | 0.39 | 0.66 | 0.04 |
| ACM101 | 4 | 229-241 | 0.52 | 2.94 | 2.37 | 0.53 | 0.56 | 0.92 | 0.06 |
| ACM132 | 11 | 186-248 | 0.67 | 5.38 | 2.78 | 0.55 | 0.61 | 1.20 | 0.09 |
| ACM138 | 5 | 242-272 | 0.66 | 3.69 | 2.82 | 0.62 | 0.61 | 1.09 | -0.02 |
| ACM147 | 2 | 264-266 | 0.37 | 1.94 | 1.83 | 0.44 | 0.44 | 0.62 | -0.01 |
| ACM152 | 4 | 228-244 | 0.25 | 2.38 | 1.41 | 0.25 | 0.27 | 0.45 | 0.07 |
| ACM235 | 4 | 286-298 | 0.41 | 2.81 | 1.77 | 0.44 | 0.41 | 0.72 | -0.06 |
| ACM446 | 6 | 108-120 | 0.56 | 3.50 | 2.48 | 0.49 | 0.58 | 1.01 | 0.16 |
| ACM449 | 8 | 120-140 | 0.66 | 4.88 | 2.82 | 0.62 | 0.61 | 1.18 | -0.03 |
| ACM463 | 5 | 202-210 | 0.47 | 3.38 | 1.95 | 0.46 | 0.48 | 0.83 | 0.05 |
| ACM504 | 2 | 188-192 | 0.33 | 1.94 | 1.64 | 0.30 | 0.37 | 0.54 | 0.20 |
| Mean | 5 | 0.48 | 3.22 | 2.15 | 0.46 | 0.48 | 0.84 | 0.05 |
집단 중에서 ARO3, ARO6, ARO8, ARO10, TRO1 및 MCO는 높은 수준의 유전적 변이(Ho > 0.5)를 나타낸 반면, 집단 ARO7(Ho = 0.27)에서 가장 낮은 다양성이 관찰되었습니다(보충 표 S2). 전반적으로 모든 액세스는 F로 표시됩니다.is XNUMX에 가까운 값(Fis 평균 값 = 0.054), 무작위 짝짓기 조건에서 예상한 대로.
분자 변이 및 유전 구조 분석
집단 간 및 집단 내에서 유전적 변이의 계층적 분할은 AMOVA에 의해 계산되었습니다. 결과는 집단 내 유전적 변이의 상당한 부분을 강조했습니다(87%). 13%의 인구 변동은 매우 중요했습니다(P < 0.001) (표 3). 0.002(ARO2/ARO10)에서 0.468(ARO7/TRO2) 범위의 Wright의 Fst 고정 지수와 유사한 Fpt 매개변수의 쌍별 값은 유의했습니다(P < 0.05), 3개의 쌍별 비교를 제외하고(보충 표 SXNUMX).
테이블 3. 320개 집단의 16개 유전자형의 분자 변이 분석 부추 속 cepa L.
| 출처 | df | 제곱의 합 | 분산 추정 | 차이(%) | Fpt | P |
| 인구 중 | 15 | 458.63 | 1.16 | 13% | ||
| 인구 내 | 304 | 2272.99 | 7.50 | 87% | 0.134 | 0.001 |
| 금액 | 319 | 2731.62 | 8.66 |
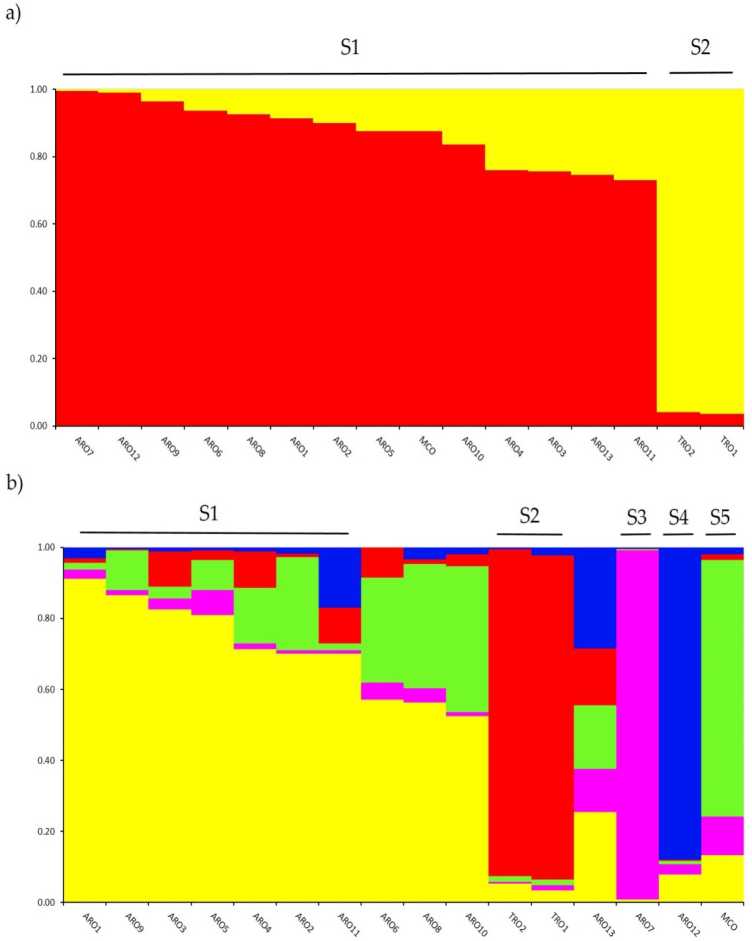
유전자 구조 조사 A. 세파 이 연구에서 유전자형이 지정된 컬렉션은 소프트웨어 STRUCTURE에서 구현된 혼합물 모델 기반 클러스터링 분석을 통해 수행되었습니다. Evanno AK 방법은 2개의 클러스터(K = XNUMX)로 세분화를 제안했습니다. 데이터 세트,일e 다음 것 최고 PEak at k = 5 (보충 Rgure 시즌1). 에이 K를 위해 = 2, a마력op에뮬레이션 w엉덩이igned 도n과f 두 클러스터 과 a rnernbertoip 계수(q) > 0.7. 에스로ho승 그림 2a, 첫 번째 클러스터(S1로 명명됨)에는 MCO 및 모든 ARO 인구가 포함된 반면 S2 클러스터는 두 개의 TRO 인구를 그룹화했습니다. K = 5에서 데이터 세트에 대한 자세한 설명을 제공합니다(그림 2b), 액세스의 75%가 1개 클러스터 중 하나에 할당되었습니다. ARO(S2)와 TRO(S0.7) 사이의 분리가 확인되었지만 일부 ARO 개체군이 혼합(q < 3)되거나 두 개의 새로운 클러스터 S4 및 S7(각각 ARO12 및 ARO5)에서 별도로 그룹화되었습니다. 흥미롭게도 MCO 상업용 유형은 Apulian red 양파에서 분리된 별개의 클러스터(SXNUMX)를 형성했습니다.
인구 간의 유전적 관계
유전적 다양성의 덴드로그램을 그릴 수 있는 SSR 다형성과 계통발생학적 분석 결과는 그림 XNUMX과 같다. 3a. 여기에서 생식질 컬렉션은 부트스트랩 값에 의해 강력하게 지원되는 7개 그룹으로 분할되었습니다. ARO12 및 AROXNUMX 개체군은 나머지 개체군과 즉시 분리되어 두 개의 별개의 클러스터를 형성했습니다. 세 번째 클러스터에는 TRO의 두 상업 집단이 포함되어 있는 반면, 네 번째 노드는 XNUMX개의 ARO 집단에서 MCO를 나눴습니다. 개체군 간에 발생하는 유전적 관계는 PCoA(주좌표 분석)를 통해 추가로 조사되었습니다(그림 3b). 이전에 강조 표시된 대로 ARO 개체군은 PCoA 플롯에서 격리된 위치에 나타나는 ARO12 및 ARO7을 제외하고 밀접하게 그룹화되었습니다. 두 개의 TRO와 MCO 모집단은 플롯의 오른쪽 아래 패널에 흩어져 있습니다.
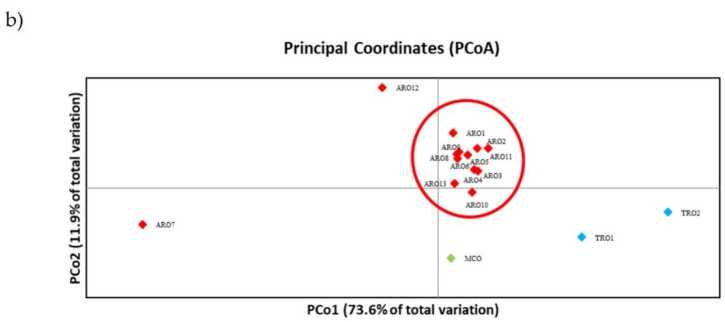
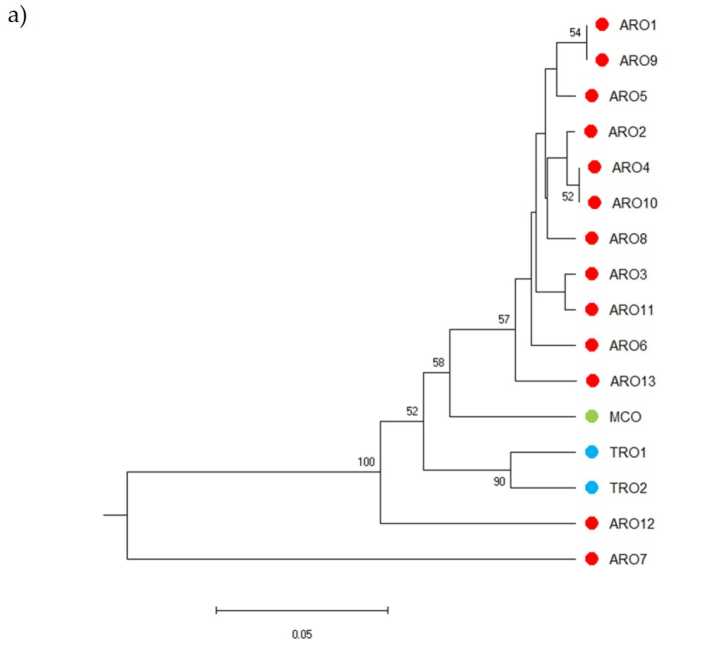
그림 3. 16명의 유전적 다양성 A. 세파 SSR 프로필을 기반으로 이 연구에서 특성화된 인구. (a) 유전적 거리의 UPGMA 덴드로그램. 부트스트랩 지원 값 >50은 해당 노드 위에 표시됩니다. (b) 주성분 분석(PCoA). 빨간색 원으로 표시된 클러스터는 계통발생학적 분석에 의해 생성된 그룹과 완전히 일치하고 11개의 ARO 접근으로 구성됩니다.
토론
남부 이탈리아에서 전통적으로 재배된 대량의 농업 생물 다양성 내에서 양파 품종은 유전적 침식의 위험과 현대 품종으로의 대체 위협으로부터 보호해야 하는 틈새 제품을 나타냅니다. 지역 유산과 밀접하게 연결된 Apulia 지역의 유전자 자원을 수집, 특성화, 홍보 및 보호하는 것을 목표로 하는 지역 프로젝트 BiodiverSO의 프레임워크에서 우리는 ARO 랜드레이스의 13개 집단의 종자 컬렉션을 설립했습니다. 우리는 DNA 다형성 및 두 가지 생화학적 매개변수인 가용성 고체 및 피루브산 함량의 관점에서 ARO 변이에 대한 첫 번째 평가를 보고했으며, 이는 풍미 특성과 관련이 있으며 신선하지 않은 제품의 수용에 중요합니다. 또한 ARO 랜드레이스에 대한 데이터는 종종 실수를 하는 XNUMX개의 다른 착색 양파 랜드레이스에서 수집된 데이터와 비교되었습니다.
생화학적 분석은 스위트 양파 산업 가이드라인에 따라 높은 가용성 고형분 함량 및 중간 매운맛과 관련된 13개 ARO 집단의 단맛을 강조했습니다. [31]. ARO 전구는 TRO 및 MCO 랜드레이스보다 달콤하고 약간 더 높은 매운맛을 나타냅니다. 그러나 양파의 단맛은 당도와 매운맛 사이의 균형 때문이므로 이 특성화는 일반적으로 형태학에만 기초하여 농부가 수행하는 가치의 유전자형 선택을 지원하는 데 유용할 수 있습니다.
SSR 마커는 Acquaviva delle Fonti 마을과 같은 좁은 재배 지역 내에서 수집되었지만 유전자형을 구별하는 유용한 도구로 확인되었습니다. 선택된 마커는 에 의해 이전에 보고된 마커보다 더 많은 수의 대립유전자를 표시했습니다. [43] 및 [44], 그러나 보고된 마커보다 낮습니다. [45]. 또한 마커 세트의 50%가 0.5보다 큰 PIC 지수 값을 보여 다음에서 제안한 것처럼 컬렉션의 인구를 구별하는 데 적합한 것으로 입증되었습니다. [46]. 인구 내 다양성 평가는 Ho와 He 사이에 유사한 값을 나타내어 Fi가 낮았습니다.s 가치. 이것은 아웃크로싱의 성격과 일치한다. A. 세파, 근친 교배 우울증으로 심각하게 고통받는 [47]. 전반적인 Fis 이 연구에서 고려된 양파 집단에서 계산된 값(0.054)은 이전에 보고된 것보다 낮았습니다. [45] (0.22)에 의해 발견된 것과 거의 동일합니다. [31] (0.08)과하면 [48] (0.00) 각각 스페인 북서부와 니제르에서 온 양파 품종의 유전적 다양성을 평가했습니다. ARO 개체군에서 주목할 만한 수준의 이형접합은 Apulia가 많은 원예 종의 다양성 센터를 나타낸다는 개념을 강화합니다. [32, 42, 49-하나].
AMOVA는 이 연구에서 유전자형이 지정된 컬렉션에서 대부분의 분자 변이가 개체군 내에 있음을 강조했습니다. 그러나 인구 집단 간의 상당한 유전적 분화(FPT 값) 유전적 계층화의 발생을 나타냈다. 사실, 우리의 결과가 대부분의 ARO 집단에서 유전적 균일성이 존재하여 잘 정의된 클러스터를 형성함을 나타내었지만, ARO7 및 ARO12 집단은 명확하게 구별되는 유전적 프로필을 보여주었습니다. 이 결과는 개체군을 채집한 두 농부가 사용한 종자의 출처가 다르기 때문일 수 있습니다. 게다가, 얻어진 결과에 기초하여, ARO 랜드레이스는 TRO 및 MCO 랜드레이스와 유전적 수준에서 명확하게 구별되는 것으로 간주될 수 있습니다. 최근 연구에서, [29] "Acquaviva", "Tropea" 및 "Montoro"를 포함한 여러 이탈리아 양파 품종의 유전적 다양성을 평가했습니다. 저자는 SNP 마커를 사용하여 더 넓은 양파 컬렉션의 유전적 다양성을 평가했지만 유전형 분석으로 "Acquaviva"를 "Tropea" 및 "Montoro" 양파와 구별할 수 없었습니다. 아마도 이 불일치는 발견된 낮은 평균 PIC 값(0.292)에 기인하며, [29]. 또한 이탈리아 군집에서 하위 구조의 존재를 조사하기 위해 나머지 컬렉션과 별도로 이탈리아 유전자형을 분석하는 것이 더 나았을 것입니다. 아마도 경험적 선택 하에서 지리적 계층이나 특성과 연결된 유전적 다양성의 패턴을 시각화할 수 있었을 것입니다.
결론적으로, 본 연구는 지역 문화 유산과 연관되어 있으며 농민들에게 경제적으로 중요한 양파 경작지에 대한 포괄적인 보고서입니다. 우리의 결과는 몇 가지 예외를 제외하고 ARO가 유전적 침식의 위험으로부터 보존될 가치가 있는 잘 정의된 유전자 풀을 특징으로 한다는 점을 강조합니다. 따라서 이 귀중한 유전적 다양성의 원천을 대표하는 컬렉션을 구축하는 것이 중요했습니다. 마지막으로, ARO의 유전적 및 표현형 특성화는 유럽 연합에서 품질 마크를 얻는 데 유용할 수 있습니다.
재료 및 방법
생식질 수집, 식물 재료 및 DNA 추출
ARO 랜드레이스의 13개 집단 세트는 Apulia 지역 프로젝트(BiodiverSO: https://www.biodiversitapuglia.it/), 이탈리아 바리 지방의 작은 아풀리아 마을인 "Acquaviva delle Fonti"에서 수행된 일련의 선교를 통해. 지리정보시스템(GIS)을 통해 각 수탁물의 수집장소를 매핑하여 표로 보고하였다. 4. 또한 TRO Landrace의 두 개체군과 MCO Landrace의 한 개체군이 본 연구에 포함되어 참조로 사용되었습니다. 모든 식물 재료는 바리 대학의 실험 농장 "P Martucci"(41° 1'22.08″ N, 16°54'25.95″ E)에서 동일한 환경 조건에서 교차 수분을 피하기 위해 보호 케이지 아래에서 재배되었습니다. 개체군 및 복파리를 통한 개체군 내 수분 보장 (루실리아 시저). 16개 집단은 구근 크기와 모양, 피부 및 살색과 관련된 특성에 대해 특성화되었습니다(표 S1). 또한, 휴대용 굴절계를 사용하여 고형물 용해도 분석을 수행하고 2,4-디니트로페닐 히드라진(0.125%)을 첨가한 양파 주스 샘플에서 매운 맛을 측정했습니다. v/v 2N의 HCl에서)에 의해 보고된 바와 같이 420 nm에서의 흡광도 평가 [31]. Duncan의 다중 범위 테스트와 SNK 테스트는 유의한 차이가 있는지 확인하기 위해 수행되었습니다.
테이블 4. 이 연구에서 수집되고 유전자형이 지정된 인구 목록. 각 개체군에 대해 식별 코드, 지역 이름, GPS 좌표 및 종자 보존 유전자 은행이 보고됩니다.
| 암호 | 성함 | GPS 좌표 | 유전자 은행 y |
| ARO1 | 치폴라 로사 디 아쿠아비바 | 40°54’21.708″ N 16°49’1.631” E | 디에스스파 |
| ARO2 | 치폴라 로사 디 아쿠아비바 | 40°53’14.28″ N 16°48’56.879” E | 디에스스파 |
| ARO3 | 치폴라 로사 디 아쿠아비바 | 40°54’11.304″ N 16°49’13.079” E | 디에스스파 |
| ARO4 | 치폴라 로사 디 아쿠아비바 | 40°54’3.348″ N 16°40’27.011” E | 디에스스파 |
| ARO5 | 치폴라 로사 디 아쿠아비바 | 40°51’59.76″ N 16°53’0.527” E | 디에스스파 |
| ARO6 | 치폴라 로사 디 아쿠아비바 | 40°52’48.72″ N 16°49’43.247” E | 디에스스파 |
| ARO7 | 치폴라 로사 디 아쿠아비바 | 40°53’13.47″ N 16°50’23.783” E | 디에스스파 |
| ARO8 | 치폴라 로사 디 아쿠아비바 | 40°53’18.816″ N 16°49’33.888” E | 디에스스파 |
| ARO9 | 치폴라 로사 디 아쿠아비바 | 40°54'51.372″ N 16°49'3.504" E | 디에스스파 |
| ARO10 | 치폴라 로사 디 아쿠아비바 | 40°54’1.188″ N 16°49’24.311” E | 디에스스파 |
| ARO11 | 치폴라 로사 디 아쿠아비바 | 40°52'49.8″ N 16°49'48.575" E | 디에스스파 |
| ARO12 | 치폴라 로사 디 아쿠아비바 | 40°52’38.892″ N 16°49’28.379” E | 디에스스파 |
| ARO13 | 치폴라 로사 디 아쿠아비바 | 40°53’21.768″ N 16°49’29.711” E | 디에스스파 |
| 트로1 | 치폴라 로사 룽가 디 트로페아 | - | 디에스스파 |
| 트로2 | 치폴라 로사 톤다 디 트로페아 | - | 디에스스파 |
| MCO | 치폴라 라마타 디 몬토로 | - | 디에스스파 |
| y Di.SSPA, 바리 대학교 토양, 식물 및 식품 과학부. |
모집단당 20개 유전자형의 잎 물질을 샘플링하여 사용할 때까지 -80°C에서 보관했습니다. 다당류가 풍부한 종의 경우 A. 세파, 다당류를 제거하는 첫 번째 단계는 양질의 DNA를 얻는 데 필수적이므로 STE 완충액(0.25M 자당, 0.03M 트리스, 0.05M EDTA)에서 초기 세척을 다음과 같이 수행했습니다. [52]. CTAB 방법에 따라 전체 DNA 추출 [53] 마지막으로 Nano Drop 2000 UV-vis 분광광도계(ThermoScientific, Waltham, MA, USA)와 0.8% 아가로스 겔 전기영동으로 품질과 농도를 확인했습니다.
SSR 분석
16가지 EST-SSR 프라이머 조합 개발 [54] 이전에 에 의해 유전적 다양성 연구에서 테스트되었습니다. [43] 및 [44] 및 21개의 게놈 SSR [45-하나] 적합성을 평가하기 위해 선별되었습니다(보충 표 S4). 각각의 forward SSR 프라이머에 M13 tail을 추가하는 경제적인 형광 태깅 방법을 사용하여 Genotyping을 수행했습니다. [56]. PCR 혼합물은 총 DNA 20ng, dNTP 혼합물 50mM, PCR 반응 완충액 0.2X, DreamTaq DNA 중합효소 1U(Thermo Scientific, Waltham, MA, USA), 역방향 프라이머 0.8gM을 포함하는 0.16gL 반응으로 제조되었습니다. , 0.032gM의 M13 서열로 확장된 정방향 프라이머(5'-TGTAAAACGACGGCCAGT-3') 및 FAM 또는 NED 형광 염료로 표지된 0.08gM의 범용 M13 프라이머(Sigma-Aldrich, St. Louis, MO, USA). PCR 반응은 대부분의 프라이머 쌍에 대해 다음 조건으로 SimpliAmp(Applied Biosystems, CA, USA) 열순환기에서 수행되었습니다: 94°C에서 5분, 40°C에서 94초, 30°C 58초 및 45°C에서 72초 및 45°C에서 72분 동안 최종 신장. ACM5 및 ACM446의 경우 터치다운 PCR을 449°C~60°C에서 55회, 10°C에서 30회 어닐링한 후 55°C에서 5분의 최종 확장을 적용했습니다. PCR 생성물을 72웰 플레이트에 로딩하고 96gL의 Hi-Di Formamide(Life Technologies, Carlsbad, CA, USA) 및 14gL GeneScan 0.5 ROX Size Standard(Life Technologies, Carlsbad, CA, USA)와 혼합했습니다. ABI PRISM 500 Avant Genetic Analyzer(Life Technologies, Carlsbad, CA, USA) 모세관 시퀀싱 기계를 사용하여 앰플리콘을 분석했으며, 여기서 대립 유전자는 공동 우성으로 점수를 매기고 GeneMapper 소프트웨어 버전 3100을 사용하여 할당했습니다.
소프트웨어 GenAlEx 6.5 [57] 및 서버스 3.0.7 [58] 대립유전자 수(Na), 유효 대립유전자 수(Ne), 관찰된 이형접합체(Ho), 예상 이형접합체(He), 다형성 정보 함량(PIC), 섀넌 정보 지수(I) 및 고정 지수(Fis)를 추정하는 데 사용되었습니다. ) 각 SSR 궤적에 대해.
유전적 다양성 평가
GenAlEx 6.5에 의해 양파 집단 간의 유전적 변이의 계층적 분할이 평가되었습니다. [57] 999 부트스트래핑으로 분자 분산 분석(AMOVA)을 통해 중요성을 테스트합니다. 또한 GenAlEx 6.5 소프트웨어를 사용하여 모든 SSR 유전자좌에 대해 Ho, He 및 Fis의 평균을 계산하여 각 개체군 내의 다양성을 추정했습니다.
모집단 구조는 STRUCTURE v.2.3.4 소프트웨어에서 구현된 베이지안 모델 기반 클러스터링 알고리즘에 의해 추론되었습니다. [59]. 데이터 세트는 1에서 10까지의 범위에 있는 다수의 가상 클러스터(K)로 실행되었으며 각 K 값당 100,000개의 독립적 실행을 설정했습니다. 각 실행에 대해 결과의 일관성을 확인하기 위해 100,000개의 초기 번인 기간과 XNUMX개의 Markov Chain Monte Carlo(MCMC) 반복이 혼합 모델 및 모집단 간의 독립 대립 유전자 빈도에서 수행되었습니다. 가장 가능성이 높은 K 값은 다음과 같이 설명된 AK 방법을 구현하여 결정되었습니다. [60], 웹 기반 프로그램 STRUCTURE HARVESTER에서 [61]. 구성원 계수(q-값)가 0.7보다 높으면 개별 인구가 특정 클러스터에 할당되고, 그렇지 않으면 혼혈 조상으로 간주됩니다.
Nei의 유전적 거리 매트릭스(보충 표 S5)에 의해 밝혀진 접근 간의 유전적 관계 패턴을 시각화하기 위해 주요 좌표 분석을 수행했습니다. 대립 유전자 빈도를 기반으로 POPTREEW 소프트웨어에서 산술 평균(UPGMA) 클러스터 분석을 사용하여 비가중 쌍 그룹 방법을 구현하여 유전적 거리의 덴드로그램을 구성했습니다. [62]. 계층적 클러스터링의 신뢰도를 평가하기 위해 부트스트래핑을 적용하여 데이터 세트의 100개 재샘플링을 설정했습니다. 마지막으로 MEGA X 소프트웨어 [63] 나무 그리기 소프트웨어로 사용되었습니다.
보충 자료: 다음은 온라인에서 사용할 수 있습니다 http://www.mdpi.com/2223-7747/9/2/260/s1. 표 S1: ARO, MCO 및 TRO 전구의 형태학적 특성. 표 S2: ARO 랜드레이스와 TRO 및 MCO 랜드레이스에 대해 계산된 이형접합 및 고정 지수. 표 S3: Fpt 매개변수의 쌍별 값. 표 S4: 연구에 사용된 SSR 목록. 표 S5. Nei 유전적 거리의 쌍별 모집단 행렬. 그림 S1: Evanno의 Delta K에 따라 변화하는 K 값의 꺾은선형 차트.
작성자 기여 : CL과 LR은 연구를 구상하고 실험을 설계했습니다. CL 및 PI는 분자 마커 분석을 수행했습니다. ARM과 VZ는 현장 시험을 수행했습니다. RM, SP, GR 및 CL은 데이터 분석에 참여했습니다. RM과 CL이 원고를 썼다. 모든 저자는 출판된 원고 버전을 읽고 동의했습니다.
기금 : 이 작업은 지역 Apulian 프로젝트 "Apulian 채소 종의 생물다양성"(Programma di Sviluppo Rurale per la Puglia 2014-2020)의 지원을 받았습니다. 미수라 10 - 소토미수라 10.2; 그랜트 CUP H92C15000270002, 이탈리아.
감사 인사 : 실험에 사용된 식물 재료를 제공한 "Azienda Agricola Iannone Anna" 및 "Associazione produttori della vera cipolla rossa di Acquaviva"에게 감사의 말을 전합니다.
이해 상충 : 저자는 아무런 이해 상충을 선언하지 않습니다.
참고자료
- 1. Stearn, WT 얼마나 많은 부추속 종들이 알려져 있습니까? 큐 매그. 1992, 9, 180-182. [CrossRef]
- 2. 파오스탯. FAO 통계 데이터베이스. 사용 가능한 온라인: http://www.fao.org/2017 (8년 2019월 XNUMX일에 액세스함).
- 3. 차단, E. 마늘과 양파의 화학. Sci. 오전. 1985, 252, 114-119. [CrossRef]
- 4. 이비; 정재호; Kim, HS 쥐의 항산화 활성에 대한 양파의 평가. 식품화학 톡시콜. 2012, 50, 3912 - 3919. [CrossRef]
- 5. 이에스엠; 문, J.; 정재호; 차용준; Shin, MJ 케르세틴이 풍부한 양파 껍질 추출물이 쥐의 동맥 혈전증에 미치는 영향. 식품화학 톡시콜. 2013, 57, 99 - 105. [CrossRef] [PubMed]
- 6. 요시나리, O.; 시오지마, Y.; Igarashi, K. zucker 당뇨병 지방 쥐에서 양파 추출물의 항 비만 효과. 영양소 2012, 4,1518 - 1526. [CrossRef]
- 7. 아카쉬, MSH; 레만, K.; Chen, S. Spice plant Allium cepa: 2형 당뇨병 치료를 위한 건강 보조 식품. 영양소 2014, 30, 1128-1137. [CrossRef] [PubMed]
- 8. 왕 Y.; Tian, WX; Ma, XF 양파의 억제효과 (부추속 세파 L.) 지방산 합성효소 억제를 통한 암세포 및 지방세포 증식에 대한 추출물. 아시아 팩. J. 암 이전. 2012,13, 5573 - 5579. [CrossRef] [PubMed]
- 9. 라이, WW; 슈, 사우스캐롤라이나; 추에, FS; 첸, YY; 양지스; 린, JP; 유치권, JC; Tsai, CH; Chung, JG Quercetin은 NF-kappaB 및 matrix metalloproteinase-2/-9 신호 전달 경로의 억제를 통해 SAS 인간 구강암 세포의 이동 및 침입을 억제합니다. 항암제 2013, 33, 1941-1950. [PubMed]
- 10. 니카스트로, HL 로스, SA; Milner, JA 마늘 및 양파: 암 예방 특성. 암 입술 2015, 8,181 - 189. [CrossRef]
- 11. Forte, L.; Torricelli, P.; 보아니니, 이.; Gazzano, M.; Rubini, K.; 피니, 엠.; Bigi, A. 케르세틴 기능화 수산화인회석의 항산화 및 뼈 복구 특성: 시험관 내 조골 세포-파골 세포-내피 세포 공동 배양 연구. 액타 바이오마터. 2016, 32, 298 - 308. [CrossRef]
- 12. Yamazaki, Y.; 이와사키, K.; M. 미카미; Yagihashi, A. XNUMX가지 부추속 채소에서 XNUMX가지 향미 전구체인 S-Alk(en)yl-L-cysteine 유도체의 분포. 식품 과학. 기술. 해상도 2011, 17, 55 - 62. [CrossRef]
- 13. 블록, E. 부추속의 유기황 화학 - 유황의 유기 화학에 대한 의미. 앙쥬. 화학 국제 에드. 영어 1992, 31, 1135-1178. [CrossRef]
- 14. Griffiths, G.; Trueman, L.; Crowther, T.; 토마스, B.; Smith, B. 양파 - 건강에 대한 세계적인 이점. 파이터. 해상도 2002,16, 603 - 615. [CrossRef]
- 15. Schwimmer, S.; Weston, WJ 매운맛의 척도로서 양파의 피루브산의 효소적 발달. J. Agric. 식품화학 1961, 9, 301 - 304. [CrossRef]
- 16. 케터, 고양이; Randle, 양파의 WM 매운맛 평가. ~ 안에 실험실 교육을 위한 검증된 연구; Karcher, SJ, Ed.; 생물학 실험실 교육 협회(ABLE): 1998년 미국 뉴욕주 뉴욕; 19권, 177-196페이지.
- 17. Hanelt, P 분류학, 진화 및 역사. ~ 안에 양파와 연합작물, Vol. I. 식물학, 생리학 및 유전학; Rabinowitch, HD, Brewster, JL, Eds.; CRC Press: Boca Raton, FL, USA, 1990; 1-26쪽.
- 18. 라비노위치, HD; 커라, L. 부추속 작물 과학: 최근 발전; CABI 출판: 영국 월링포드, 2002.
- 19. Mallor, C.; Carravedo, M.; 에스토파난, G.; Mallor, F. 양파의 유전자원 특성화 (부추속 세파 L.) 다양성의 스페인어 보조 센터에서. 기간. J. Agric. 해상도 2011, 9, 144-155. [CrossRef]
- 20. F. 페리올리; D'Antuono, 이탈리아와 우크라이나의 현지 양파 및 샬롯 생식질에서 페놀 및 시스테인 설폭사이드의 LF 평가. 그 가죽. 자원. 작물 진화 2016, 63, 601 - 614. [CrossRef]
- 21. Petropoulos, SA; 페르난데스, A.; Barros, L.; 페레이라, ICFR; Ntatsi, G. 그리스에서 온 양파 토종종인 'vatikiotiko'의 형태학적, 영양학적, 화학적 설명. 식품화학 2015,182, 156-163. [CrossRef]
- 22. Liguori, L.; Adiletta, G.; 나자로, F.; Fratianni, F.; 디 마테오, M.; Albanese, D. 지중해 지역에서 다양한 양파 품종의 생화학적, 항산화 특성 및 항균 활성. J. 식품 측정. 캐릭터. 2019,13, 1232-1241. [CrossRef]
- 23. 유우경; 파이크, 엘.; Crosby, K.; 존스, R.; Leskovar, D. 품종, 성장 환경 및 구근 크기로 인한 양파 매운맛의 차이. 과학. 호틱. 2006,110, 144-149. [CrossRef]
- 24. 비스크, N.; Perner, H.; Schwarz, D.; 조지, E.; Kroh, LW; Rohn, S. 유전자형의 영향을 받는 양파 구근(Allium cepa L.)의 다른 부분에서 케르세틴-3, 4'-O-디글루코시드, 케르세틴-4'-O-모노글루코시드 및 케르세틴의 분포. 식품화학 2010,122, 566 - 571. [CrossRef]
- 25. Caruso, G.; Conti, S.; 빌라리, G.; Borrelli, C.; 멜키오나, G.; 미누톨로, M.; Russo, G.; Amalfitano, C. 양파의 수확량, 품질 및 항산화 함량에 대한 이식 시간 및 식물 밀도의 영향 (부추속 세파 L.) 이탈리아 남부. 과학. 호틱. 2014,166, 111-120. [CrossRef]
- 26. Perez-Gregorio, MR; Regueiro, J.; Simal-Gandara, J.; 로드리게스, AS; Almeida, DPF 항산화 플라보노이드 공급원으로서 양파의 부가가치 증가: 비판적 리뷰. 크리티컬 Food Sci. Nutr. 2014, 54,1050 - 1062. [CrossRef] [PubMed]
- 27. Pohnl, T.; 슈바이거트, RM; Carle, R. 양파의 가용성 탄수화물 및 매운 원리에 대한 재배 방법 및 품종 선택의 영향 (부추속 세파 엘.). J. Agric. 식품화학 2018, 66, 12827-12835. [CrossRef] [PubMed]
- 28. 테데스코, I.; Carbone, V.; Spagnuolo, C.; 미나시, P.; Russo, GL XNUMX개의 남부 이탈리아 품종의 플라보노이드 식별 및 정량 부추 속 cepa L., Tropea(적양파) 및 Montoro(구리 양파), 그리고 산화 스트레스로부터 인간 적혈구를 보호하는 능력. J. Agric. 식품화학 2015, 63, 5229 - 5238. [CrossRef]
- 29. 빌라노, C.; 에스포지토, 에스.; 카루치, F.; Frusciante, L.; Carputo, D.; Aversano, R. 양파의 고처리량 유전형은 유전적 다양성의 구조와 분자 육종에 유용한 유익한 SNP를 보여줍니다. 몰. 새끼를 낳다. 2019, 39, 5. [CrossRef]
- 30. 메르카티, F.; Longo, C.; 포마, D.; 아라니티, F.; 루피니, A.; 맘마노, MM; 피오레, MC; 아베나볼리, MR; Sunseri, F 이탈리아 장기 보관 토마토의 유전자 변이 (Solanum lycopersicum L.) SSR 및 형태학적 과일 특성을 사용하여 수집합니다. 그 가죽. 자원. 작물 진화 2014, 62, 721 - 732. [CrossRef]
- 31. Gonzalez-Perez, S.; Mallor, C.; Garces-Claver, A.; 메리노, F.; 타보아다, A.; 리베라, A.; 포마르, F.; Perovic, D.; Silvar, C. 양파 컬렉션의 유전적 다양성과 품질 특성 탐색 (부추속 세파 L.) 스페인 북서부에서 온 토지 인종. 유전학 2015, 47, 885 - 900. [CrossRef]
- 32. 로티, C.; Iovieno, P.; 센토마니, I.; 마르코트리지아노, AR; Fanelli, V.; Mimiola, G.; Summo, C.; 파반, 에스.; Ricciardi, L. 케일의 유전적, 생물농경학적, 영양학적 특성화(브라 시카 올레 라 케아 L. var. 아세팔라) 남부 이탈리아 Apulia의 다양성. 다양성 2018,10, 25. [CrossRef]
- 33. Bardaro, N.; 마르코트리지아노, AR; 브라쿠토, V.; Mazzeo, R.; Ricciardi, F.; 로티, C.; 파반, 에스.; Ricciardi, L. 저항성 유전자 분석 오로반체 크레나타 (포스크.) 완두콩 (피섬 사티붐 L.) 낮은 스트리고락톤 라인. J. 식물 경로. 2016, 98, 671 - 675.
- 34. Wako, T.; 츠카자키, H.; Yaguchi, S.; Yamashita, K.; 이토 S.; Shigyo, M. 양파 다발에서 볼팅 시간에 대한 정량적 형질 유전자좌 매핑 (부추속 누관 엘.). 유피티카 2016, 209, 537 - 546. [CrossRef]
- 35. N. 다카; Mukhopadhyay, A.; Paritosh, K.; 굽타, V.; Pental, D.; Pradhan, AK 유전자 SSR 식별 및 SSR 기반 연결 맵 구축 브라시카 윤시아. 유피티카 2017, 213, 15. [CrossRef]
- 36. Anandhan, S.; 모트, SR; Gopal, J. SSR 마커를 사용한 양파 품종 동일성 평가. 종자 과학. 기술. 2014, 42, 279 - 285. [CrossRef]
- 37. Mitrova, K.; Svoboda, P.; Ovesna, J. 체코 공화국의 양파 품종 구별을 위한 마커 세트의 선택 및 검증. 체코 J. Genet. 식물 품종. 2015, 51, 62 - 67. [CrossRef]
- 38. 디 리엔조, V.; 미아찌, MM; Fanelli, V.; 사베타, 더블유.; Montemurro, C. Apulian 올리브 생식질 생물 다양성의 보존 및 특성화. 액타 호르틱. 2018,1199,1 - 6. [CrossRef]
- 39. Mallor, C.; Arnedo-Andres, A.; Garces-Claver, A. 스페인어의 유전적 다양성 평가 부추 속 cepa microsatellite 마커를 사용하여 양파 육종을 위한 Landraces. 과학. 호틱. 2014,170, 24-31. [CrossRef]
- 40. 리베라, A.; Mallor, C.; Garces-Claver, A.; Garcia-Ulloa, A.; 포마르, F.; Silvar, C. 양파의 유전적 다양성 평가(부추 속 cepa L.) 스페인 북서부 지역과 유럽의 다양성과의 비교. NZJ 크롭 호틱. 2016, 44, 103-120. [CrossRef]
- 41. De Giovanni, C.; 파반, 에스.; 타란토, F.; 디 리엔조, V.; 미아찌, MM; 마르코트리지아노, AR; Mangini, G.; 몬테무로, C.; Ricciardi, L.; Lotti, C. 병아리콩의 글로벌 생식질 컬렉션의 유전적 변이 (사이서 에티늄 L.) 유전적 침식의 위험에 처한 이탈리아 계통을 포함합니다. 생리. 몰. 바이올. 식물 2017, 23, 197-205. [CrossRef]
- 42. Mazzeo, R.; 모르지스, A.; Sonnante, G.; 줄루아가, DL; 파반, 에스.; Ricciardi, L.; Lotti, C. 브로콜리 라베의 유전적 다양성 (브라시카 라파 L. subsp. 실베스트리 스 (L.) Janch.) 남부 이탈리아에서. 과학. 호틱. 2019, 253, 140-146. [CrossRef]
- 43. Jakse, M.; 마틴, 더블유.; McCallum, J.; Havey, M. 양파 품종 식별을 위한 단일 뉴클레오티드 다형성, 삽입결실 및 단순 서열 반복. 제이엠 사회 호틱. 과학. 2005,130, 912 - 917. [CrossRef]
- 44. McCallum, J.; Thomson, S.; Pither-Joyce, M.; Kenel, F. 발현된 서열 태그-단순 서열 반복 마커를 기반으로 한 재배 전구 양파의 유전적 다양성 분석 및 단일 뉴클레오티드 다형성 마커 개발. 제이엠 사회 호틱. 과학. 2008,133, 810 - 818. [CrossRef]
- 45. Baldwin, S.; Pither-Joyce, M.; 라이트, K.; 첸, 엘.; McCallum, J. 전구 양파 내부 및 간의 유전적 다양성 평가를 위한 강력한 게놈 단순 서열 반복 마커의 개발 (부추속 세파 L.) 인구. 몰. 새끼를 낳다. 2012, 30, 1401-1411. [CrossRef]
- 46. DeWoody, JA; 허니컷, RL; Skow, LC 흰 꼬리 사슴의 Microsatellite 마커. J. 헤레드. 1995, 86, 317 - 319. [CrossRef] [PubMed]
- 47. Khodadadi, M.; Hassanpanah, D.이란 양파 (부추속 세파 L.) 근친 교배 우울증에 대한 품종 반응. 세계 응용 프로그램. 과학. 제이. 2010,11, 426 - 428.
- 48. Abdou, R.; 바카소, Y.; 사두, M.; 보두인, JP; Hardy, OJ 니제르 양파의 유전적 다양성 (부추속 세파 L.) 단순 서열 반복 마커(SSR)에 의해 평가. 액타 호르틱. 2016,1143, 77 - 90. [CrossRef]
- 49. Pavan, S.; 로티, C.; 마르코트리지아노, AR; Mazzeo, R.; Bardaro, N.; 브라쿠토, V.; Ricciardi, F.; 타란토, F.; D'Agostino, N.; Schiavulli, A.; et al. 게놈 전체의 마커 발견 및 유전형 분석에 의해 밝혀진 재배 병아리콩의 뚜렷한 유전적 클러스터. 식물 게놈 2017, 2017,10. [CrossRef]
- 50. Pavan, S.; 마르코트리지아노, AR; Ciani, E.; Mazzeo, R.; Zonno, V.; Ruggieri, V.; 로티, C.; Ricciardi, L. 멜론의 유전자형 분석 (쿠쿠미스 멜로 L.) 다양성의 XNUMX차 센터로부터의 생식질 수집은 다양한 유전자 풀의 유전적 변이 및 게놈 특징의 패턴을 강조합니다. BMC 게놈. 2017, 18, 59. [CrossRef]
- 51. 디 리엔조, V.; 시온, 에스.; 타란토, F.; D'Agostino, N.; 몬테무로, C.; Fanelli, V.; 사베타, 더블유.; Boucheffa, S.; Tamendjari, A.; Pasqualone, A.; et al. 지중해 분지 내 올리브 개체군의 유전적 흐름. 피어 J. 2018, 6. [CrossRef]
- 52. 셰퍼드, LD; McLay, TG 다당류가 풍부한 식물 조직에서 DNA를 분리하기 위한 두 가지 마이크로 규모 프로토콜. J. 식물 해상도. 2011,124, 311 - 314. [CrossRef]
- 53. Doyle, JJ; Doyle, JL 신선한 조직에서 식물 DNA 분리. 초점 1990,12, 13-14.
- 54. Kuhl, JC; 청에프; Qiaoping, Y.; 마틴, 더블유.; Zewdie, Y.; McCallum, J.; 카타나흐, A.; Rutherford, P.; 싱크, KC; Jenderek, M.; et al. 11,008개의 고유한 양파 발현 서열 태그 세트는 단자엽 아스파라갈레와 가금류 사이의 발현된 서열 및 게놈 차이를 나타냅니다. 식물 세포 2004,16, 114 - 125. [CrossRef]
- 55. 김혜진; 이인사; 현정이; 송경호; 김경호; 김제; 허, 씨지; Harn, SSR Finder를 이용한 양파 유전자 순도 검사용 CH Marker 개발. 한국 제이 품종. 과학. 2012, 44, 421 - 432. [CrossRef]
- 56. Schuelke, M. PCR 단편의 형광 표지를 위한 경제적인 방법. Nat. 바이오 테크 놀. 2000, 18, 233 - 234. [CrossRef] [PubMed]
- 57. Peakall, R.; Smouse, PE GenAlEx 6.5: Excel에서 유전자 분석. 교육 및 연구를 위한 인구 유전 소프트웨어: 업데이트. 생물 정보학 2012, 28, 2537 - 2539. [CrossRef] [PubMed]
- 58. 칼리노프스키, ST; 테이퍼, ML; Marshall, TC 컴퓨터 프로그램 CERVUS가 유전자형 오류를 수용하는 방법을 수정하면 친자 지정의 성공률이 높아집니다. 몰. 에코. 2007,16, 1099-1106. [CrossRef]
- 59. 프리차드, JK; 스티븐스, 엠.; 로젠버그, NA; Donnelly, P. 구조화된 모집단의 협회 매핑. 이다. J. 흠. 그 가죽. 2000, 67, 170 - 181. [CrossRef]
- 60. Evanno, G.; 레그넛, 에스.; Goudet, J. 소프트웨어를 사용하여 개인의 클러스터 수 감지: 구조: 시뮬레이션 연구. 몰. 에코. 2005,14, 2611 - 2620. [CrossRef]
- 61. 얼, D.; VonHoldt, B. STRUCTURE HARVESTER: STRUCTURE 출력을 시각화하고 Evanno 방법을 구현하기 위한 웹사이트 및 프로그램입니다. 보존 그 가죽. 자원. 2011, 4. [CrossRef]
- 62. Takezaki, N.; Nei, M.; Tamura, K. POPTREEW: 대립유전자 빈도 데이터로부터 모집단 트리를 구성하고 다른 수량을 계산하기 위한 POPTREE의 웹 버전. 몰. 바이올. 진화 2014, 31, 1622 - 1624. [CrossRef]
- 63. Kumar, S.; Stecher, G.; 리, 엠.; 크냐즈, C.; Tamura, K. MEGA X. 컴퓨팅 플랫폼 전반에 걸친 분자 진화 유전학 분석. 몰. 바이올. 진화 2018, 35, 1547-1549. [CrossRef]